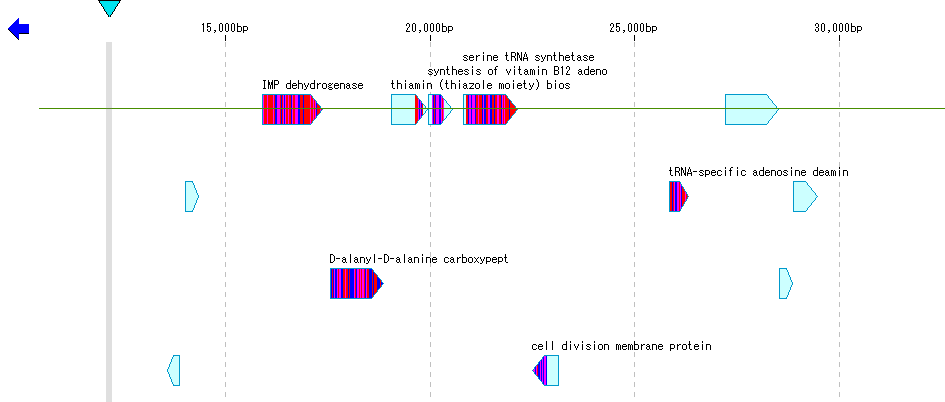
メインフィーチャーマップ の フィーチャーレーン の選択領域に含まれる CDS フィーチャーを クエリー配列 として、Blast を使用した ホモロジー検索 を実行します。
ホモロジー検索結果は各フィーチャーの Qualifier に記録されます。
これらのQualifierを使用して、フィーチャー の形状、カラー、ラベル などをそれらに従って表示することができます。
操作
- コーディング領域 が同定されており、CDSフィーチャーとして登録されているゲノム配列を カレントフィーチャーマップ にロードします。
- カレント参照ディレクトリ には、サンプルデータ として E_coli.gbk と S_typhimurium.gbk をロードしておきます。
- マウスをドラッグして、Blast検索 を実行する領域を選択します。
- 選択領域 上でマウス右クリックします。
- メニューが表示されます。
- 「Homology Search by Selected Feature」をクリックします。
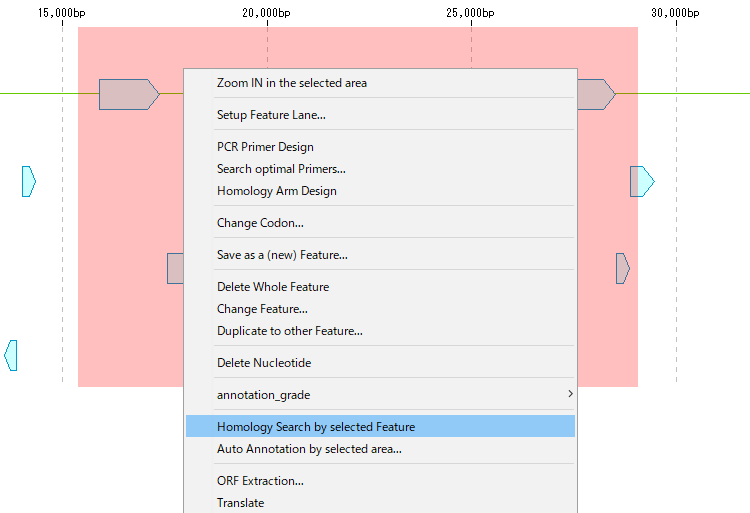
- 「Batch Homology Setting」ダイアログが表示されます。
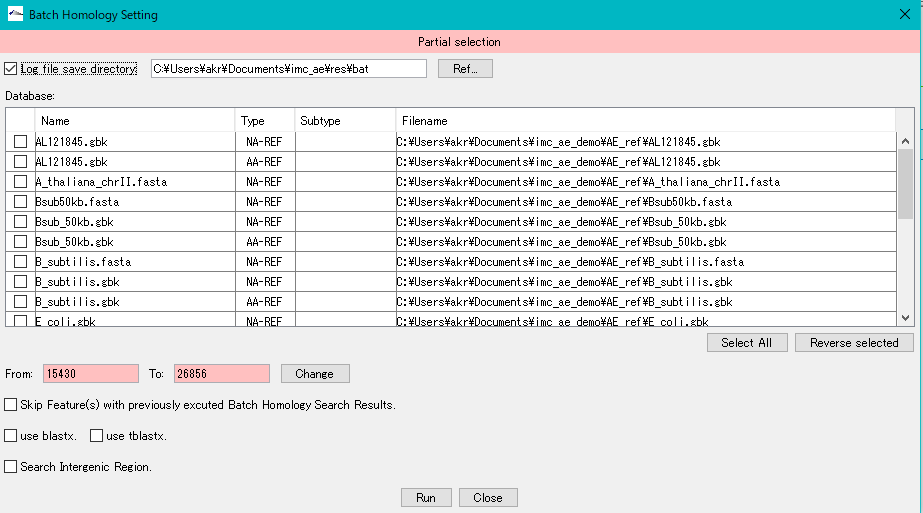
- カレントレファレンスディレクトリ にロードされているゲノム配列の塩基配列とアミノ酸配列が Blast検索用データベース として選択できるようになっています。
- この他にも 検索用データベース を作成し、ここにリストアップすることができます。(こちら)
- ここでは、例として、E_coli.gbkの AA-REF とS_typhimurium.gbkのAA-REFをチェックし、検索用データベースとします。
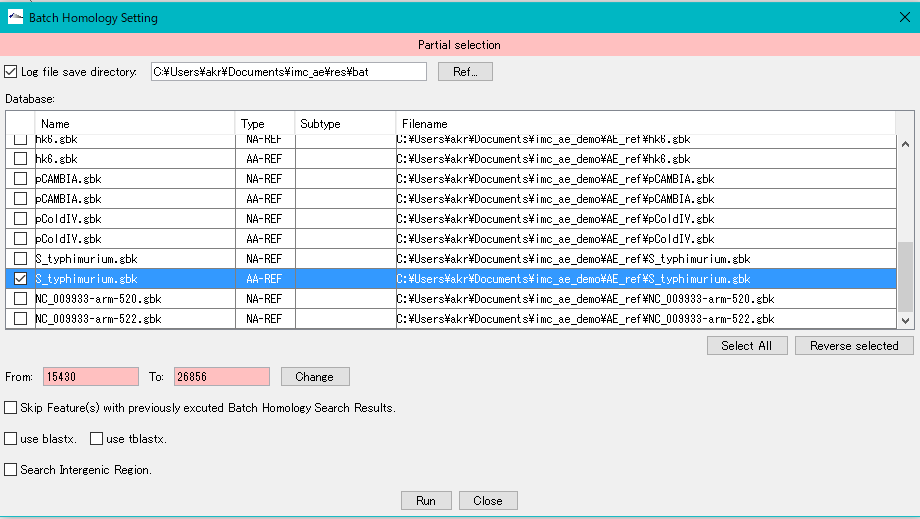
- 「Run」をクリックします。
- 「Start Homology Search?」実行確認ダイアログ が表示されます。
- 「Show Parameter…」をクリックします。
- 実行確認ダイアログが拡大し表示され、Blast検索実行パラメータ が表示されます。
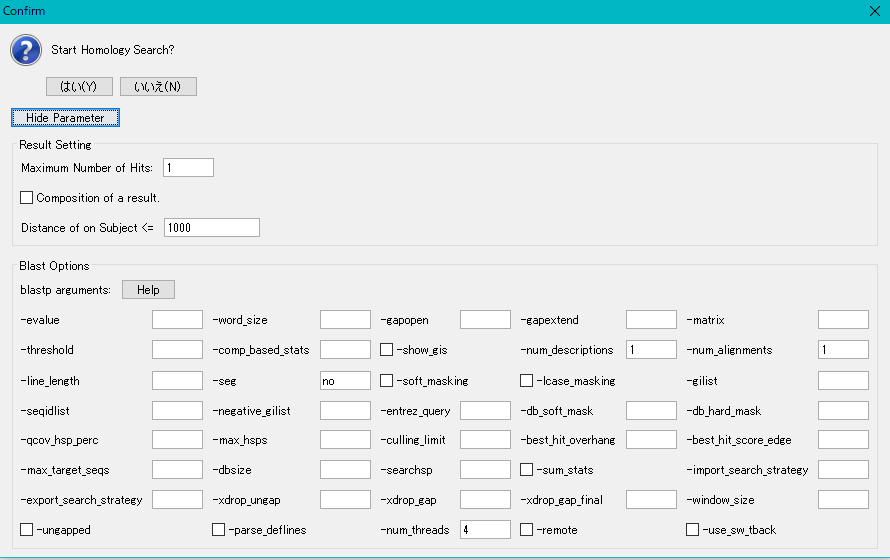
- 「Result Setting 欄の「Maximum Number of Hits」入力フィールドに 最大ヒット数 を正の整数で直接入力します。
- これは、クエリー 毎にいくつの検索結果を保存するかを指定します。
- 入力した数値以上のヒットは保存されませんが、ヒット数が少ない場合などは、この数値をより少ないヒットが保存されます。
- ここでは、これを5に設定します。
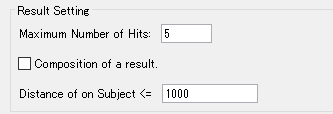
- 「はい(Y)」をクリックします。
- Blast検索の実行が開始されます。
- 実行中は、進捗メッセージ が表示されます。
- 検索が終了すると、検索結果ダイアログ が表示されます。
- このダイアログから 手動アノテーション を実行できます(説明はこちら)。
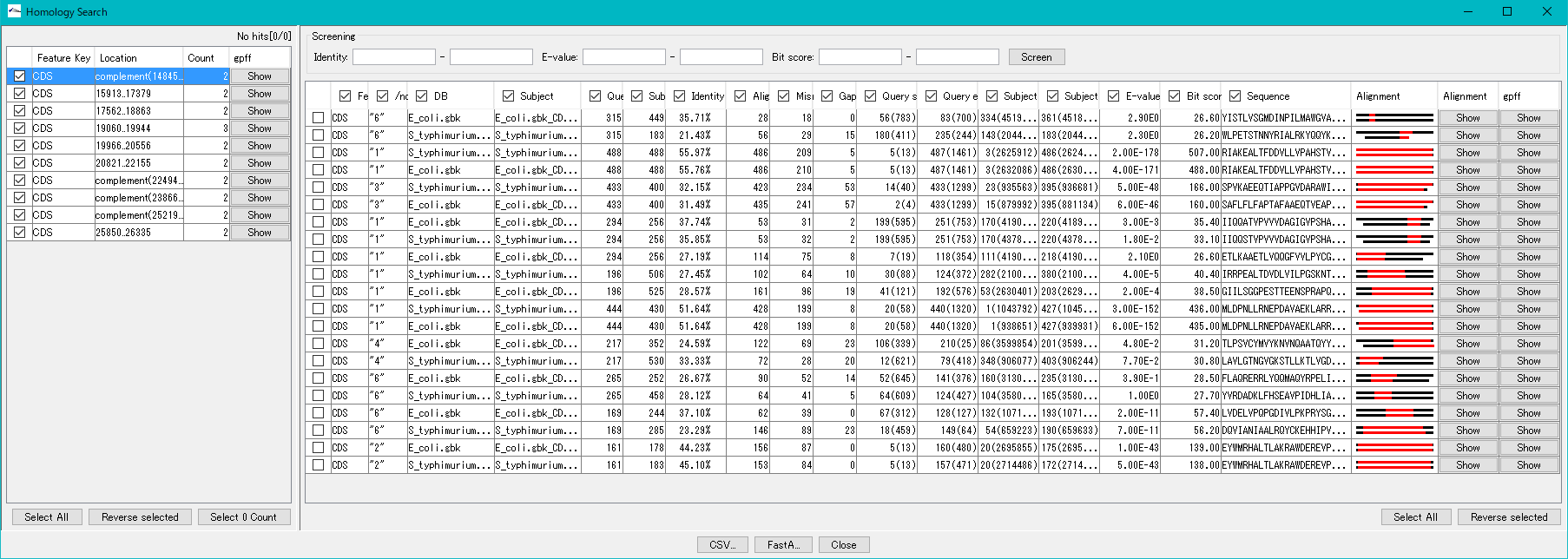
- 「Auto Copy]が設定されている場合は、トップヒット のQualifierの指定されたものが自動的に クエリーCDS に登録されます。
- 「Auto Copy」の説明はこちらです。
- 検索結果ダイアログからは手動アノテーションできます。手動アノテーションはこちら。
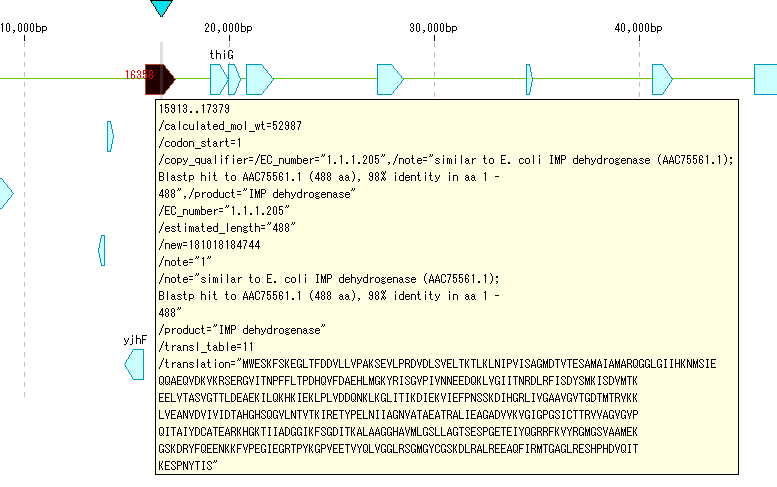
- 自動転記 された結果を閲覧します。
- Toolbox からラベルボタンをオンにします。CDSフィーチャーの上にラベルが表示されます。
- 下の場合は、gene がラベルとされています。
- ラベルボタン をオフにします。
- CDSフィーチャーの上のラベルが消えます。
- ラベルボタンをオフにしてもラベルが消えない場合は、そのラベルが「Permanent Label」となっているためです。
- これを解除するには、「Feature Setting」ダイアログの「Feature Map」タブペイン からその設定を変更する必要があります。
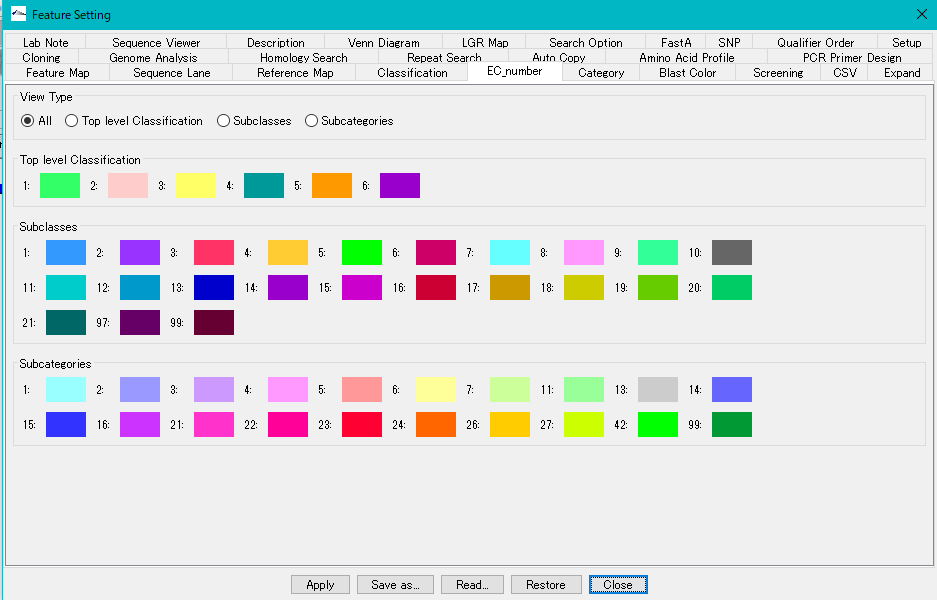
- Toolboxから「EC」ボタンをクリックします。
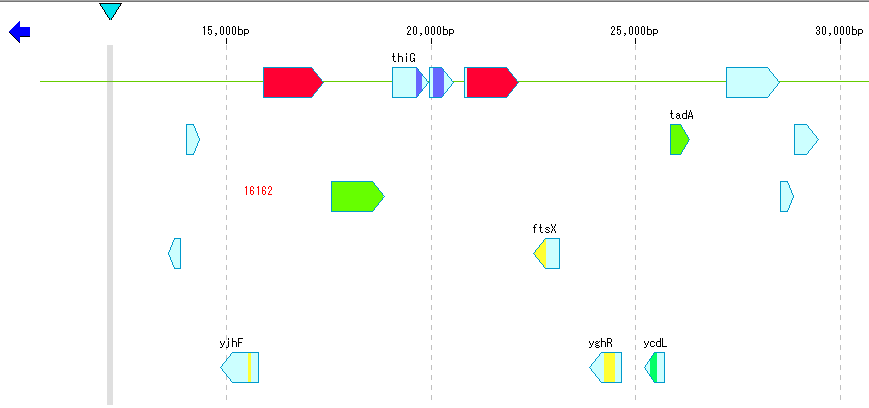
- EC番号 を転記されたCDSは EC番号 に割り当てられたカラーで表示されます。
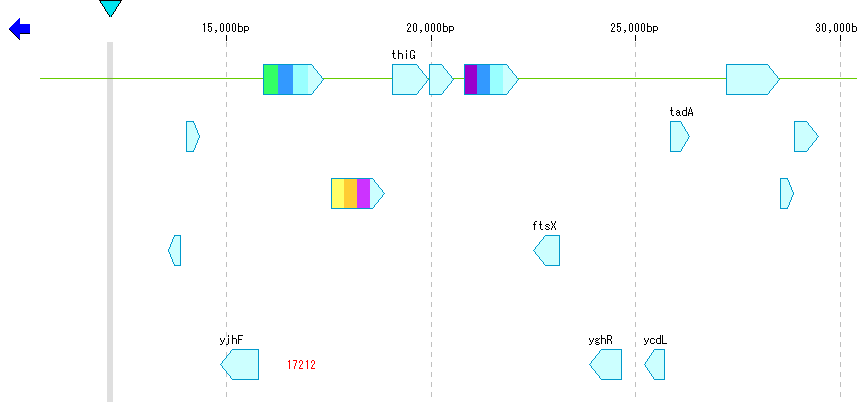
- このカラー設定は、「EC_number」タブペインで変更できます。
- ToolBoxから「BL」ボタンをクリックします。
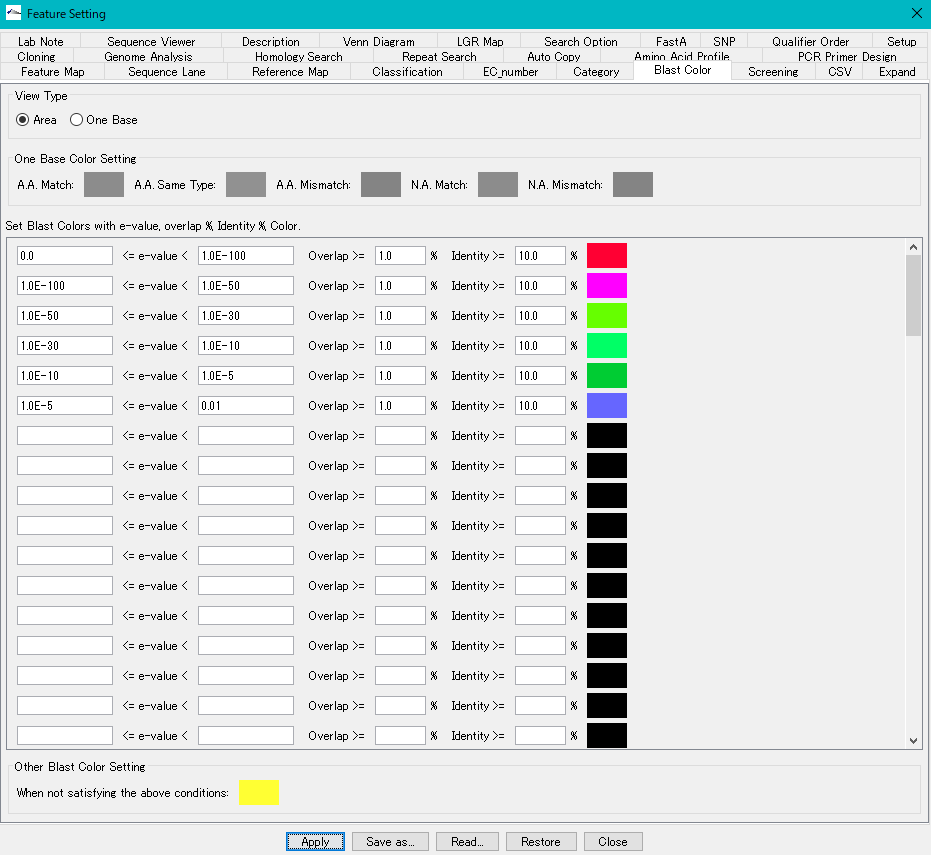
- ヒットしたCDSフィーチャーは Blastスコアカラー で表示されます。
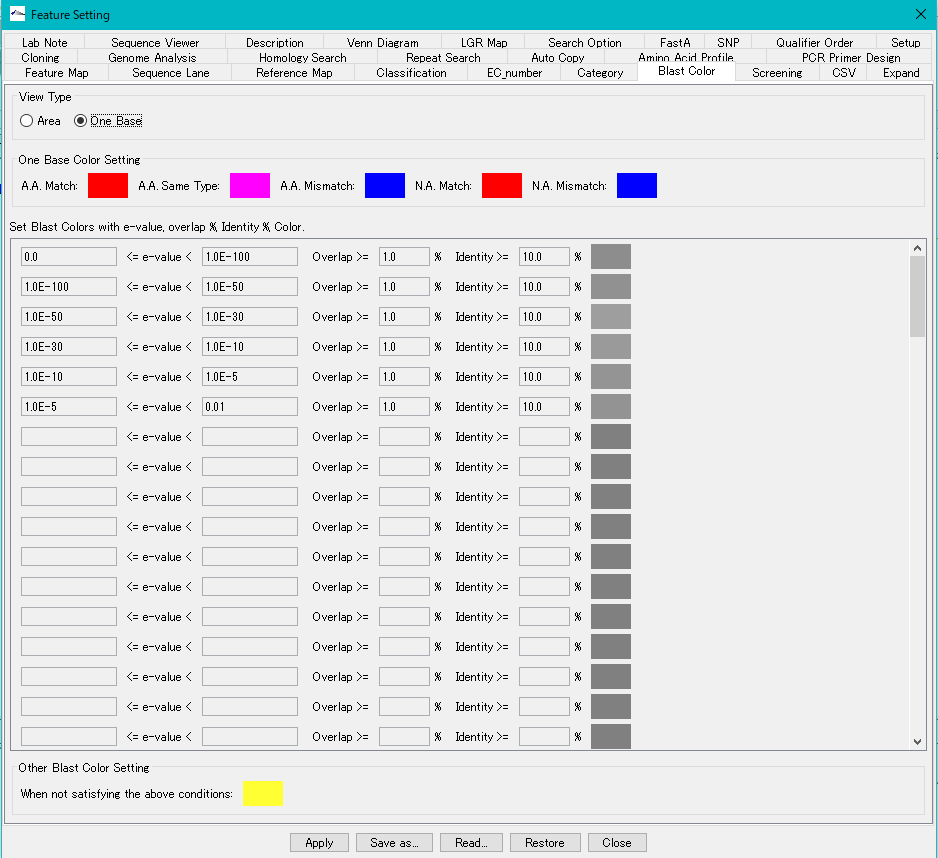
- このカラーの設定は、「Blast Color」タブペインで変更できます。
- Blastスコアカラーは ヒット領域 別で表示されますが、アミノ酸残基 単位、あるいは 塩基単位 でのカラー表示も可能です。
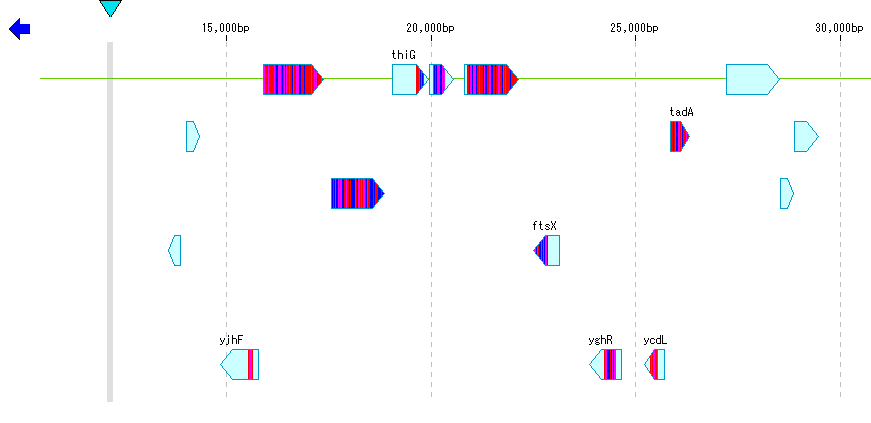
- このカラー設定は、「Blast Color」タブペインで変更できます。
ラベルとして使用するQualifierを変更する場合は「Feature Map」から変更します。- 「gene」から「product」に変更します。
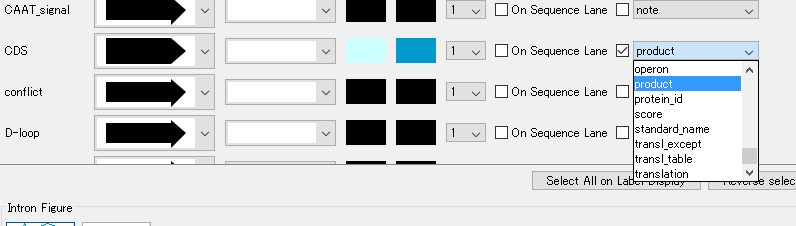
- ラベルとして、CDSフィーチャーのQualifier「product」が使用されています。
